Contar vecinos en contacto#
En este notebook visualizamos qué células en un tejido son vecinas dibujando una malla. Además, podemos cambiar la intensidad de la malla para que se corresponda con la distancia entre los centroides de las células.
import pyclesperanto_prototype as cle
import numpy as np
import pandas as pd
Datos de prueba#
Vamos a generar una estructura similar a un tejido que consiste en células que típicamente tienen aproximadamente 6 vecinos.
cells = cle.artificial_tissue_2d(
delta_x=48,
delta_y=32,
random_sigma_x=7,
random_sigma_y=7,
width=250,
height=250)
cle.imshow(cells, labels=True)

Malla entre células vecinas#
Antes de contar los vecinos, deberíamos visualizar las relaciones de vecindad. Podemos hacer esto dibujando una malla entre los centroides de las células vecinas que se tocan.
mesh = cle.draw_mesh_between_touching_labels(cells)
cle.imshow(mesh)

También podemos combinar ambas visualizaciones en una sola imagen. Ten en cuenta que estas imágenes no deben usarse más adelante para análisis cuantitativos. Solo sirven para propósitos de visualización.
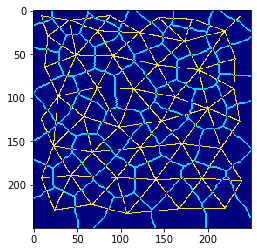
Conexiones de centroides y bordes celulares#
Una forma común de visualizar tejidos en este contexto es dibujando los bordes celulares y la malla de centroides en diferentes colores.
visualization = mesh * 2 + cle.detect_label_edges(cells)
cle.imshow(visualization, color_map='jet')
Analizar y visualizar el número de vecinos en contacto#
También podemos contar los vecinos en contacto y visualizar el resultado como una imagen paramétrica en colores.
neighbor_count_image = cle.touching_neighbor_count_map(cells)
cle.imshow(neighbor_count_image, color_map='jet', colorbar=True, min_display_intensity=0)

Ten en cuenta que los números a lo largo del borde de la imagen pueden no ser precisos. Por lo tanto, deberíamos excluir las células correspondientes del análisis posterior.
cells_ex_border = cle.exclude_labels_on_edges(cells)
cle.imshow(cells_ex_border, labels=True)

Después de corregir la imagen de etiquetas, también podemos corregir la imagen paramétrica.
neighbor_count_image_ex_border = neighbor_count_image * (cells_ex_border != 0)
cle.imshow(neighbor_count_image_ex_border, color_map='jet', colorbar=True, min_display_intensity=0)

Ahora, podemos medir el número de vecinos. Podemos simplemente leer esos números y ponerlos en una lista …
cle.read_intensities_from_map(cells_ex_border, neighbor_count_image_ex_border)
cl.Array([[0., 5., 6., 7., 6., 6., 7., 6., 6., 5., 5., 6., 6., 7., 6., 6.,
6., 6., 6., 6., 6.]], dtype=float32)
… también podemos leer estos valores junto con todas las demás estadísticas y ponerlos en un DataFrame de pandas.
statistics = cle.statistics_of_labelled_pixels(neighbor_count_image_ex_border, cells_ex_border)
table = pd.DataFrame(statistics)
# renombrar una columna
table = table.rename(columns={"mean_intensity": "number_of_neighbors"})
# filtrar solo un subconjunto de todas las columnas; solo lo que nos interesa
table = table[["label", "number_of_neighbors", "centroid_x", "centroid_y"]]
table
| label | number_of_neighbors | centroid_x | centroid_y | |
|---|---|---|---|---|
| 0 | 1 | 5.0 | 74.592697 | 23.731028 |
| 1 | 2 | 6.0 | 173.741379 | 35.582230 |
| 2 | 3 | 7.0 | 49.460915 | 51.928082 |
| 3 | 4 | 6.0 | 91.783768 | 52.666199 |
| 4 | 5 | 6.0 | 142.728210 | 62.962471 |
| 5 | 6 | 7.0 | 189.973206 | 68.526794 |
| 6 | 7 | 6.0 | 73.699181 | 88.797356 |
| 7 | 8 | 6.0 | 115.321083 | 90.665649 |
| 8 | 9 | 5.0 | 163.097733 | 99.824242 |
| 9 | 10 | 5.0 | 58.206852 | 122.341309 |
| 10 | 11 | 6.0 | 98.847565 | 134.280228 |
| 11 | 12 | 6.0 | 147.731705 | 127.326218 |
| 12 | 13 | 7.0 | 200.522903 | 112.817368 |
| 13 | 14 | 6.0 | 67.880905 | 162.991592 |
| 14 | 15 | 6.0 | 122.943306 | 157.515717 |
| 15 | 16 | 6.0 | 171.010025 | 153.333328 |
| 16 | 17 | 6.0 | 43.426266 | 189.492981 |
| 17 | 18 | 6.0 | 96.272728 | 192.326477 |
| 18 | 19 | 6.0 | 140.815964 | 194.446030 |
| 19 | 20 | 6.0 | 193.817596 | 193.019318 |
Ejercicio#
Analiza un campo de visión más grande con más células y varía los parámetros random_sigma_x y random_sigma_y de la función artificial_tissue_2d. Utiliza un mapa de conteo de vecinos en contacto para contar el número de vecinos en contacto antes y después de aplicar un filtro de mediana al mapa.
