Medición de intensidad en los bordes de etiquetas#
En algunas aplicaciones, es razonable medir la intensidad en los bordes de las etiquetas. Por ejemplo, para medir la intensidad de la señal en una imagen que muestra la envoltura nuclear, se pueden segmentar los núcleos, identificar sus bordes y luego medir la intensidad allí.
import numpy as np
from skimage.io import imread, imshow
import pyclesperanto_prototype as cle
from cellpose import models, io
from skimage import measure
import matplotlib.pyplot as plt
2022-02-24 10:05:10,405 [INFO] WRITING LOG OUTPUT TO C:\Users\rober\.cellpose\run.log
El conjunto de datos de ejemplo#
En este ejemplo, cargamos una imagen que muestra un ojo de pez cebra, cortesía de Mauricio Rocha Martins, laboratorio Norden, MPI CBG Dresden.
multichannel_image = imread("../../data/zfish_eye.tif")
multichannel_image.shape
(1024, 1024, 3)
cropped_image = multichannel_image[200:600, 500:900]
nuclei_channel = cropped_image[:,:,0]
cle.imshow(nuclei_channel)
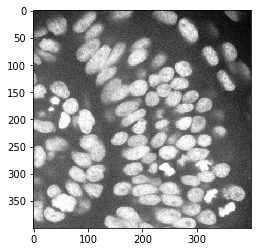
Segmentación de imagen#
Primero, usamos cellpose para segmentar las células
# cargar modelo cellpose
model = models.Cellpose(gpu=False, model_type='nuclei')
# aplicar modelo
channels = [0,0] # Esto significa que estamos procesando imágenes en escala de grises de un solo canal.
label_image, flows, styles, diams = model.eval(nuclei_channel, diameter=None, channels=channels)
# mostrar resultado
cle.imshow(label_image, labels=True)
2022-02-24 10:05:10,623 [INFO] >>>> using CPU
2022-02-24 10:05:10,675 [INFO] ~~~ ESTIMATING CELL DIAMETER(S) ~~~
2022-02-24 10:05:13,858 [INFO] estimated cell diameter(s) in 3.18 sec
2022-02-24 10:05:13,859 [INFO] >>> diameter(s) =
2022-02-24 10:05:13,860 [INFO] [ 29.64 ]
2022-02-24 10:05:13,860 [INFO] ~~~ FINDING MASKS ~~~
2022-02-24 10:05:18,649 [INFO] >>>> TOTAL TIME 7.97 sec
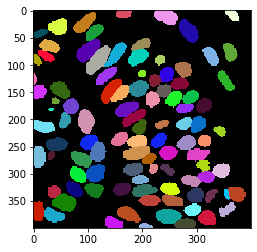
Etiquetado de píxeles en los bordes de las etiquetas#
A continuación, extraeremos el contorno de los núcleos segmentados.
binary_borders = cle.detect_label_edges(label_image)
labeled_borders = binary_borders * label_image
cle.imshow(label_image, labels=True)
cle.imshow(binary_borders)
cle.imshow(labeled_borders, labels=True)
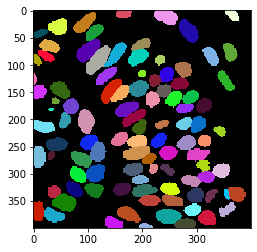

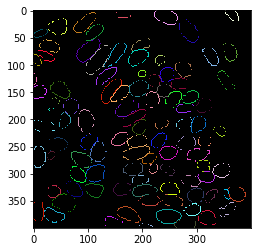
Dilatación de contornos#
Extendemos los contornos un poco para tener una medición más robusta.
extended_outlines = cle.dilate_labels(labeled_borders, radius=2)
cle.imshow(extended_outlines, labels=True)
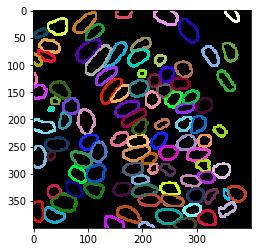
Visualización superpuesta#
Usando esta imagen de etiquetas de contornos nucleares, podemos medir la intensidad en la envoltura nuclear.
nuclear_envelope_channel = cropped_image[:,:,2]
cle.imshow(nuclear_envelope_channel)
cle.imshow(nuclear_envelope_channel, alpha=0.5, continue_drawing=True)
cle.imshow(extended_outlines, alpha=0.5, labels=True)

Estadísticas de intensidad de etiquetas#
La medición de la intensidad en la imagen funciona usando las imágenes correctas de intensidad y etiquetas.
stats = cle.statistics_of_labelled_pixels(nuclear_envelope_channel, extended_outlines)
stats["mean_intensity"]
array([35529.4 , 32835.07 , 36713.887, 37146.348, 49462.39 , 36392.6 ,
37998.375, 48974.945, 31805.87 , 50451.793, 41006.047, 50854.016,
36167.547, 41332.32 , 37815.766, 35121.38 , 43859.945, 40292.875,
31583.992, 38933.57 , 32297.547, 39140.766, 37072.31 , 45990.57 ,
39800.613, 37804.99 , 39092.43 , 39510.848, 40534.81 , 42057.293,
44815.844, 42855.754, 38408.246, 41257.594, 37996.895, 38568.465,
42331.266, 34748.973, 44219.844, 41986.086, 38606.215, 39008.094,
36411.05 , 48155.797, 43781.97 , 38315.12 , 36048.39 , 37739.277,
46268.816, 35808.32 , 37388.312, 37682.21 , 42932.72 , 38168.293,
40489.73 , 43073.066, 40973.285, 40975.246, 39292.848, 38555.766,
38219.785, 40054.242, 37356.87 , 45014.8 , 37211.668, 47025.47 ,
30218.678, 33988.027, 37338.41 , 38500.85 , 38546.777, 40611.742,
40391.453, 41024.46 , 37840.246, 41342.793, 39329.625, 43311.016,
37829.074, 39949.82 , 39316.496, 40966.48 , 34066.7 , 34929.863,
40356.445, 31959.607, 39480.855, 39194.027, 46274.582, 31316.648,
37623.61 , 40962.016, 39203.37 , 45368.703, 37830.832, 35296.93 ,
37756.1 , 39108.93 , 40739.543], dtype=float32)
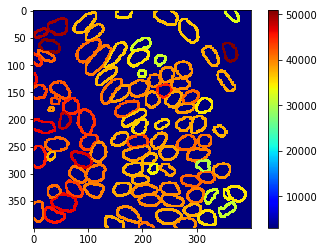
Mapas paramétricos#
Estas mediciones también se pueden visualizar utilizando mapas paramétricos
intensity_map = cle.mean_intensity_map(nuclear_envelope_channel, extended_outlines)
cle.imshow(intensity_map, min_display_intensity=3000, colorbar=True, colormap="jet")
Ejercicio#
Mide y visualiza la intensidad en los bordes de las etiquetas en el canal de núcleos.
