Bordes de etiquetas
Cuando se procesan objetos biológicos en imágenes como células y núcleos, puede tener sentido identificar todos los píxeles que se encuentran en la superficie de un objeto.
Este cuaderno demuestra cómo seleccionar píxeles en el borde de los núcleos, en caso de que quisiéramos medir la intensidad en la envoltura nuclear.

|
cle._ image
| shape | (40, 40) |
| dtype | float32 |
| size | 6.2 kB |
| min | 12.0 | | max | 255.0 |

|
Luego segmentamos los núcleos.

|
cle._ image
| shape | (40, 40) |
| dtype | uint32 |
| size | 6.2 kB |
| min | 0.0 | | max | 4.0 |
|
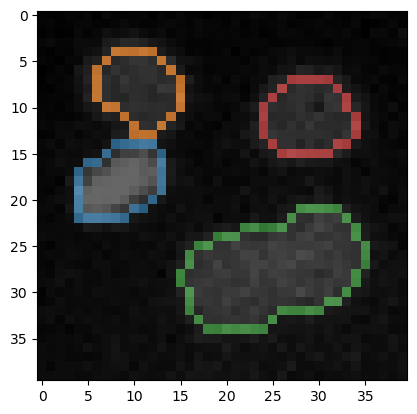
A partir de la imagen de etiquetas de los núcleos, podemos extraer otra imagen de etiquetas que contiene todos los píxeles que están en el borde de las etiquetas.

|
cle._ image
| shape | (40, 40) |
| dtype | uint32 |
| size | 6.2 kB |
| min | 0.0 | | max | 4.0 |
|
En caso de que se quisiera medir en áreas más gruesas a lo largo de los bordes, podríamos expandir los bordes.

|
cle._ image
| shape | (40, 40) |
| dtype | uint32 |
| size | 6.2 kB |
| min | 0.0 | | max | 4.0 |
|
Para fines de visualización, también podemos ver la imagen original con los bordes de las etiquetas superpuestos.