Définitions de voisinage#
Dans pyclesperanto, les graphes d’adjacence des voisins sont utilisés pour étudier les relations entre les objets étiquetés voisins, tels que les cellules. Ce notebook démontre les définitions de voisinage considérées.
Voir aussi
import pyclesperanto_prototype as cle
import numpy as np
import matplotlib
from numpy.random import random
cle.select_device("RTX")
<NVIDIA GeForce RTX 3050 Ti Laptop GPU on Platform: NVIDIA CUDA (1 refs)>
Pour visualiser les relations entre les objets voisins, nous commençons par une grille de cellules artificielle. Les cellules sont alignées approximativement dans une grille en nid d’abeille. L’intensité dans ces cellules est uniformément répartie. Seule une cellule au centre de la grille a une intensité beaucoup plus élevée.
# Generate artificial cells as test data
tissue = cle.artificial_tissue_2d()
# fill it with random measurements
values = random([int(cle.maximum_of_all_pixels(tissue))])
for i, y in enumerate(values):
if (i != 95):
values[i] = values[i] * 10 + 45
else:
values[i] = values[i] * 10 + 90
measurements = cle.push(np.asarray([values]))
# visualize measurments in space
example_image = cle.replace_intensities(tissue, measurements)
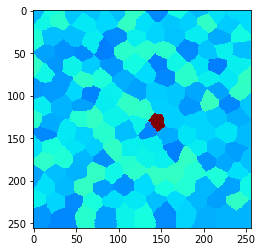
Données d’exemple#
Jetons un coup d’œil à une image avec des pixels de forme arbitraire. Appelons-les “cellules”. Dans notre image d’exemple, il y a une cellule au centre avec une intensité plus élevée :
cle.imshow(example_image, min_display_intensity=30, max_display_intensity=90, color_map='jet')
Voisins en contact#
Nous pouvons montrer toutes les cellules qui appartiennent au voisinage “en contact” en visualisant le graphe des voisins en contact sous forme de maillage.
mesh = cle.draw_mesh_between_touching_labels(tissue)
# make lines a bit thicker for visualization purposes
mesh = cle.maximum_sphere(mesh, radius_x=1, radius_y=1)
cle.imshow(mesh)

Si nous appliquons un filtre de maximum local à cette grille, nous pouvons voir comment l’intensité élevée de la cellule unique au centre se propage aux cellules voisines en contact direct.
local_maximum = cle.maximum_of_touching_neighbors_map(example_image, tissue)
cle.imshow(local_maximum, min_display_intensity=30, max_display_intensity=90, color_map='jet')

Voisins des voisins en contact#
Vous pouvez également étendre le voisinage en considérant les voisins des voisins (des voisins (des voisins)). La portée de cette extension peut être configurée avec un paramètre de rayon.
Rayon==0 signifie qu’aucun voisin n’est pris en compte,
rayon==1 est identique aux voisins en contact,
rayon > 1 correspond aux voisins des voisins.
for radius in range(0, 5):
local_maximum = cle.maximum_of_touching_neighbors_map(example_image, tissue, radius=radius)
cle.imshow(local_maximum, min_display_intensity=30, max_display_intensity=90, color_map='jet')





N voisins les plus proches#
Vous pouvez également définir un voisinage à partir des distances entre les cellules. Comme mesure de distance, nous utilisons la distance euclidienne entre les centroïdes des étiquettes. Dans ce cas également, vous pouvez configurer la portée du voisinage en définissant le nombre de voisins les plus proches n. Comme mentionné ci-dessus, les voisinages incluent la cellule centrale. Ainsi, le voisinage d’un objet et de son n=1 voisin le plus proche contient deux voisins.
for n in range(1, 10):
print("n = ", n)
mesh = cle.draw_mesh_between_n_closest_labels(tissue, n=n)
# make lines a bit thicker for visualization purposes
mesh = cle.maximum_sphere(mesh, radius_x=1, radius_y=1)
cle.imshow(mesh)
n = 1

n = 2

n = 3

n = 4

n = 5

n = 6

n = 7

n = 8

n = 9

Cela peut également être visualisé en utilisant le filtre de maximum local. Par rapport aux voisins des voisins, le rayon du voisinage peut être ajusté plus finement en utilisant les n voisins les plus proches. Notez que pour calculer le maximum dans ce voisinage, toute augmentation de n += 1 n’augmente pas nécessairement la taille de la zone rouge. Cela est dû au fait que ce n’est pas le pixel maximum qui pousse son intensité vers les voisins, mais les voisins qui tirent cette intensité lors de l’application du filtre maximum.
for n in range(1, 10):
print("n = ", n)
local_maximum = cle.maximum_of_n_nearest_neighbors_map(example_image, tissue, n=n)
cle.imshow(local_maximum, min_display_intensity=30, max_display_intensity=90, color_map='jet')
n = 1

n = 2

n = 3

n = 4

n = 5

n = 6

n = 7

n = 8

n = 9

Voisins proximaux#
Nous pouvons également calculer le maximum local des cellules dont les distances entre centroïdes sont inférieures à un seuil supérieur donné.
local_maximum = cle.maximum_of_proximal_neighbors_map(example_image, tissue, max_distance=20)
cle.imshow(local_maximum, min_display_intensity=30, max_display_intensity=90, color_map='jet')

local_maximum = cle.maximum_of_proximal_neighbors_map(example_image, tissue, max_distance=50)
cle.imshow(local_maximum, min_display_intensity=30, max_display_intensity=90, color_map='jet')

Exercice#
Dessinez un maillage entre les voisins proximaux avec différentes distances, par exemple dans une boucle for.
