Bords des étiquettes
Lors du traitement d’objets biologiques dans une image tels que les cellules et les noyaux, il peut être judicieux d’identifier tous les pixels qui se trouvent à la surface d’un objet.
Ce notebook montre comment sélectionner les pixels sur le bord des noyaux, au cas où nous voudrions mesurer l’intensité dans l’enveloppe nucléaire.

|
cle._ image
| shape | (40, 40) |
| dtype | float32 |
| size | 6.2 kB |
| min | 12.0 | | max | 255.0 |

|
Nous segmentons ensuite les noyaux.

|
cle._ image
| shape | (40, 40) |
| dtype | uint32 |
| size | 6.2 kB |
| min | 0.0 | | max | 4.0 |
|
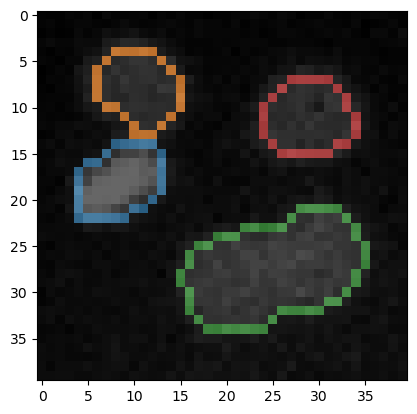
À partir de l’image étiquetée des noyaux, nous pouvons extraire une autre image étiquetée qui contient tous les pixels se trouvant sur le bord des étiquettes.

|
cle._ image
| shape | (40, 40) |
| dtype | uint32 |
| size | 6.2 kB |
| min | 0.0 | | max | 4.0 |
|
Au cas où on voudrait mesurer dans des zones plus épaisses le long des bords, nous pourrions élargir les bords.

|
cle._ image
| shape | (40, 40) |
| dtype | uint32 |
| size | 6.2 kB |
| min | 0.0 | | max | 4.0 |
|
À des fins de visualisation, nous pouvons également voir l’image originale avec les bordures des étiquettes superposées.