(image-segmentation:voronoi-otsu-labeling=)
Étiquetage de Voronoi-Otsu#
Ce flux de travail pour la segmentation d’image est une approche plutôt simple et pourtant puissante, par exemple pour détecter et segmenter les noyaux dans les images de microscopie à fluorescence. Un marqueur de noyaux tel que le GFP nucléaire, le DAPI ou l’histone-RFP en combinaison avec diverses techniques de microscopie peut être utilisé pour générer des images de type approprié.
from skimage.io import imread, imshow
import matplotlib.pyplot as plt
import pyclesperanto_prototype as cle
import napari_segment_blobs_and_things_with_membranes as nsbatwm
Pour démontrer le flux de travail, nous utilisons des données d’image du Broad Bio Image Challenge : Nous avons utilisé l’ensemble d’images BBBC022v1 Gustafsdottir et al., PLOS ONE, 2013, disponible dans la Collection de référence de bio-images du Broad Ljosa et al., Nature Methods, 2012.
input_image = imread("../../data/BBBC022/IXMtest_A02_s9.tif")[:,:,0]
input_crop = input_image[0:200, 200:400]
fig, axs = plt.subplots(1, 2, figsize=(15, 15))
cle.imshow(input_image, plot=axs[0])
cle.imshow(input_crop, plot=axs[1])
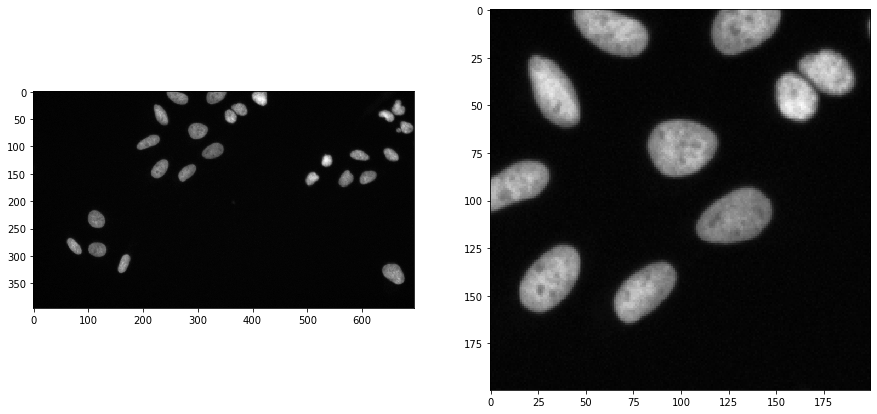
Application de l’algorithme#
L’étiquetage de Voronoi-Otsu est une commande dans clesperanto, qui demande deux paramètres sigma. Le premier sigma contrôle la proximité des cellules détectées (spot_sigma) et le second contrôle la précision du contour des objets segmentés (outline_sigma).
sigma_spot_detection = 5
sigma_outline = 1
segmented = cle.voronoi_otsu_labeling(input_image, spot_sigma=sigma_spot_detection, outline_sigma=sigma_outline)
segmented_crop = segmented[0:200, 200:400]
fig, axs = plt.subplots(1, 2, figsize=(15, 15))
cle.imshow(segmented, labels=True, plot=axs[0])
cle.imshow(segmented_crop, labels=True, plot=axs[1])
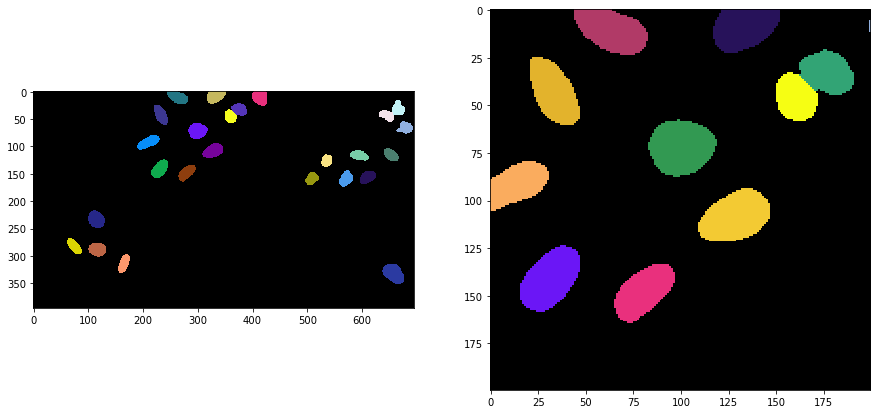
Autres implémentations de l’étiquetage Voronoi-Otsu#
Il existe une implémentation alternative de l’algorithme dans le plugin napari scriptable napari-segment-blobs-and-things-with-membranes.
Le code ici est presque identique au code ci-dessus. La principale différence est que nous appelons nsbatwm.voronoi_otsu_labeling() au lieu de cle.voronoi_otsu_labeling().
sigma_spot_detection = 5
sigma_outline = 1
segmented2 = nsbatwm.voronoi_otsu_labeling(input_image, spot_sigma=sigma_spot_detection, outline_sigma=sigma_outline)
segmented_crop2 = segmented2[0:200, 200:400]
fig, axs = plt.subplots(1, 2, figsize=(15, 15))
cle.imshow(segmented2, labels=True, plot=axs[0])
cle.imshow(segmented_crop2, labels=True, plot=axs[1])


Comment ça marche ?#
Le flux de travail d’étiquetage Voronoi-Otsu est une combinaison de flou gaussien, de détection de spots, de seuillage et de watershed binaire. Le lecteur intéressé peut consulter le code source ouvert. L’approche est similaire à l’application d’un watershed avec graines à une image binaire, par exemple dans MorphoLibJ ou scikit-image. Cependant, les graines sont calculées automatiquement et ne peuvent pas être transmises.
À des fins de démonstration, nous ne le faisons que sur l’image 2D recadrée montrée ci-dessus. Si cet algorithme est appliqué à des données 3D, il est recommandé de les rendre d’abord isotropes.
Dans une première étape, nous floutons l’image avec un sigma donné et détectons les maxima dans l’image résultante.
De plus, nous repartons de l’image recadrée et la floutons à nouveau, avec un sigma différent. Ensuite, nous seuillons l’image en utilisant la méthode de seuillage d’Otsu (Otsu et al 1979).
Ensuite, nous prenons l’image binaire des spots et l’image binaire de segmentation et appliquons une opération
binary_andpour exclure les spots qui ont été détectés dans la zone d’arrière-plan. Ceux-ci correspondaient probablement à du bruit.Ensuite, nous séparons l’espace de l’image entre les spots sélectionnés en utilisant un diagramme de Voronoi qui est limité aux pixels positifs de l’image binaire.