Mesure de l’intensité sur les bordures des étiquettes#
Dans certaines applications, il est raisonnable de mesurer l’intensité sur les bordures des étiquettes. Par exemple, pour mesurer l’intensité du signal dans une image montrant l’enveloppe nucléaire, on peut segmenter les noyaux, identifier leurs bordures et ensuite mesurer l’intensité à ces endroits.
import numpy as np
from skimage.io import imread, imshow
import pyclesperanto_prototype as cle
from cellpose import models, io
from skimage import measure
import matplotlib.pyplot as plt
2022-02-24 10:05:10,405 [INFO] WRITING LOG OUTPUT TO C:\Users\rober\.cellpose\run.log
L’ensemble de données d’exemple#
Dans cet exemple, nous chargeons une image montrant un œil de poisson zèbre, avec l’aimable autorisation de Mauricio Rocha Martins, laboratoire Norden, MPI CBG Dresden.
multichannel_image = imread("../../data/zfish_eye.tif")
multichannel_image.shape
(1024, 1024, 3)
cropped_image = multichannel_image[200:600, 500:900]
nuclei_channel = cropped_image[:,:,0]
cle.imshow(nuclei_channel)
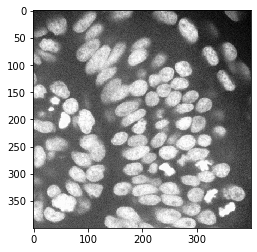
Segmentation d’image#
D’abord, nous utilisons cellpose pour segmenter les cellules
# load cellpose model
model = models.Cellpose(gpu=False, model_type='nuclei')
# apply model
channels = [0,0] # This means we are processing single channel greyscale images.
label_image, flows, styles, diams = model.eval(nuclei_channel, diameter=None, channels=channels)
# show result
cle.imshow(label_image, labels=True)
2022-02-24 10:05:10,623 [INFO] >>>> using CPU
2022-02-24 10:05:10,675 [INFO] ~~~ ESTIMATING CELL DIAMETER(S) ~~~
2022-02-24 10:05:13,858 [INFO] estimated cell diameter(s) in 3.18 sec
2022-02-24 10:05:13,859 [INFO] >>> diameter(s) =
2022-02-24 10:05:13,860 [INFO] [ 29.64 ]
2022-02-24 10:05:13,860 [INFO] ~~~ FINDING MASKS ~~~
2022-02-24 10:05:18,649 [INFO] >>>> TOTAL TIME 7.97 sec
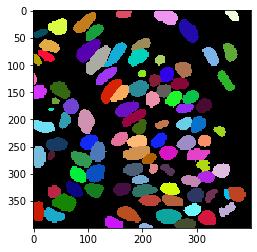
Étiquetage des pixels sur les bordures des étiquettes#
Ensuite, nous allons extraire le contour des noyaux segmentés.
binary_borders = cle.detect_label_edges(label_image)
labeled_borders = binary_borders * label_image
cle.imshow(label_image, labels=True)
cle.imshow(binary_borders)
cle.imshow(labeled_borders, labels=True)
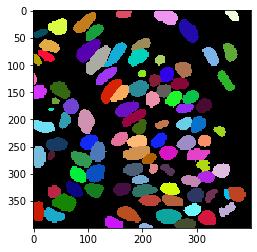

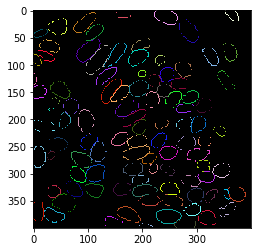
Dilatation des contours#
Nous étendons un peu les contours pour avoir une mesure plus robuste.
extended_outlines = cle.dilate_labels(labeled_borders, radius=2)
cle.imshow(extended_outlines, labels=True)
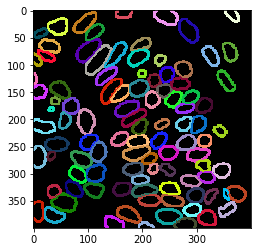
Visualisation en superposition#
En utilisant cette image d’étiquettes des contours des noyaux, nous pouvons mesurer l’intensité dans l’enveloppe nucléaire.
nuclear_envelope_channel = cropped_image[:,:,2]
cle.imshow(nuclear_envelope_channel)
cle.imshow(nuclear_envelope_channel, alpha=0.5, continue_drawing=True)
cle.imshow(extended_outlines, alpha=0.5, labels=True)

Statistiques d’intensité des étiquettes#
La mesure de l’intensité dans l’image fonctionne en utilisant les bonnes images d’intensité et d’étiquettes.
stats = cle.statistics_of_labelled_pixels(nuclear_envelope_channel, extended_outlines)
stats["mean_intensity"]
array([35529.4 , 32835.07 , 36713.887, 37146.348, 49462.39 , 36392.6 ,
37998.375, 48974.945, 31805.87 , 50451.793, 41006.047, 50854.016,
36167.547, 41332.32 , 37815.766, 35121.38 , 43859.945, 40292.875,
31583.992, 38933.57 , 32297.547, 39140.766, 37072.31 , 45990.57 ,
39800.613, 37804.99 , 39092.43 , 39510.848, 40534.81 , 42057.293,
44815.844, 42855.754, 38408.246, 41257.594, 37996.895, 38568.465,
42331.266, 34748.973, 44219.844, 41986.086, 38606.215, 39008.094,
36411.05 , 48155.797, 43781.97 , 38315.12 , 36048.39 , 37739.277,
46268.816, 35808.32 , 37388.312, 37682.21 , 42932.72 , 38168.293,
40489.73 , 43073.066, 40973.285, 40975.246, 39292.848, 38555.766,
38219.785, 40054.242, 37356.87 , 45014.8 , 37211.668, 47025.47 ,
30218.678, 33988.027, 37338.41 , 38500.85 , 38546.777, 40611.742,
40391.453, 41024.46 , 37840.246, 41342.793, 39329.625, 43311.016,
37829.074, 39949.82 , 39316.496, 40966.48 , 34066.7 , 34929.863,
40356.445, 31959.607, 39480.855, 39194.027, 46274.582, 31316.648,
37623.61 , 40962.016, 39203.37 , 45368.703, 37830.832, 35296.93 ,
37756.1 , 39108.93 , 40739.543], dtype=float32)
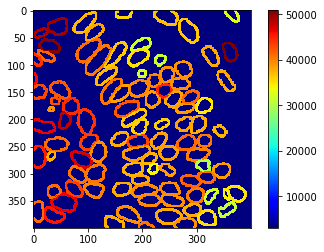
Cartes paramétriques#
Ces mesures peuvent également être visualisées à l’aide de cartes paramétriques
intensity_map = cle.mean_intensity_map(nuclear_envelope_channel, extended_outlines)
cle.imshow(intensity_map, min_display_intensity=3000, colorbar=True, colormap="jet")
Exercice#
Mesurez et visualisez l’intensité aux bordures des étiquettes dans le canal des noyaux.
